Mica Le premier Microhub d’imagerie au monde.
Plus qu’un microscope hautement automatisé, le Mica réunit l’imagerie confocale et en champ large dans un environnement d’incubation et de protection des échantillons.
Vous pouvez désormais vous concentrer sur votre science, et non plus sur le fonctionnement de votre microscope.
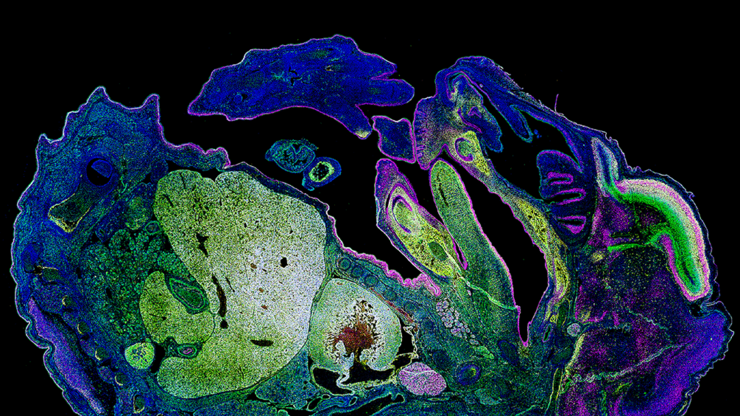
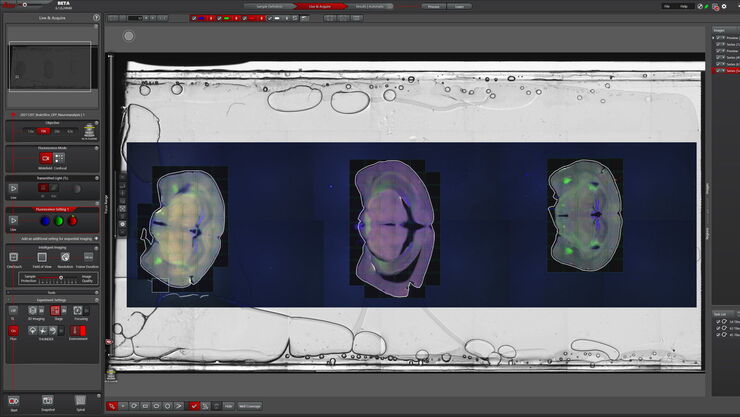
Nous travaillons avec des organoïdes du cancer du pancréas. Ainsi, dès que nous identifions des structures intéressantes et souhaitons zoomer tout en disposant d'une résolution plus élevée, nous passons du mode épifluorescence au mode confocal d'un seul clic.
Aucune contrainte - 4 fois plus de données avec une corrélation de 100 %.
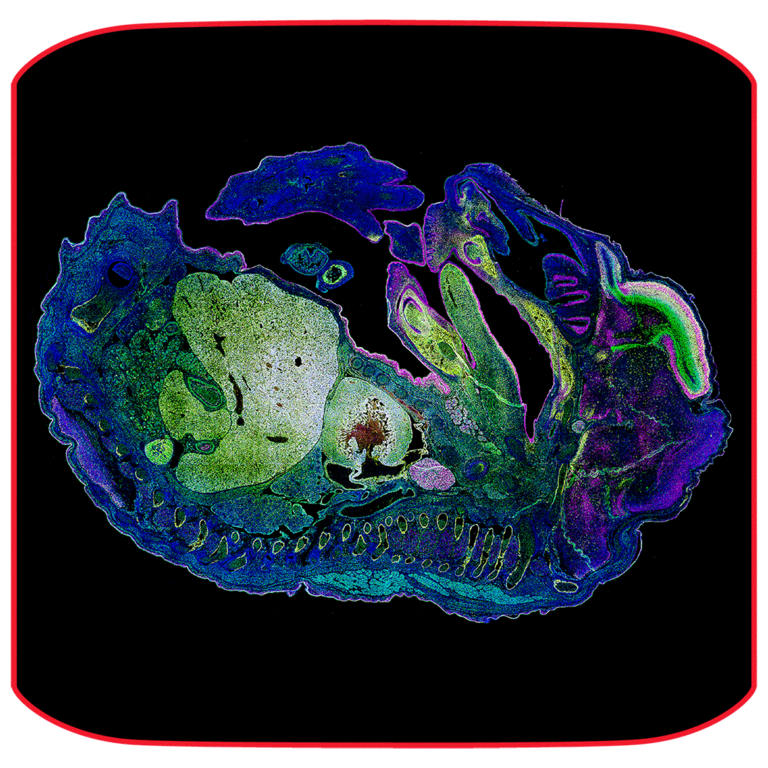
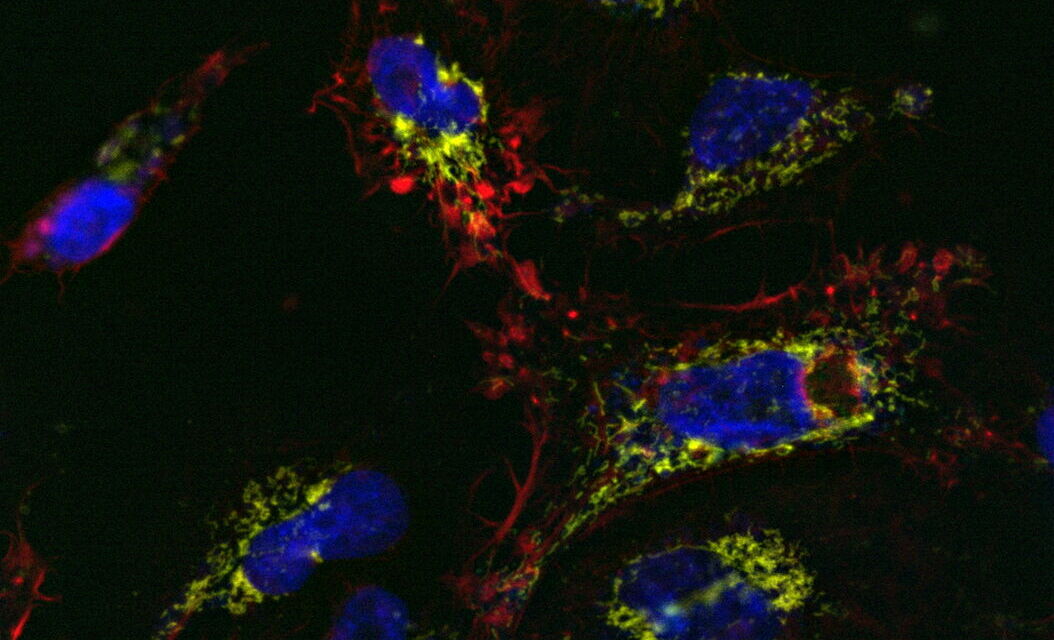
Le Microhub vous permet de capturer simultanément les 4 marqueurs ou différentes structures en une seule acquisition en champ large et confocal, sans jamais déplacer votre échantillon. Cela permet de remédier au décalage spatio-temporel entre les marqueurs des objets en mouvement lors de l’acquisition séquentielle.
Aucune contrainte - Sélectionnez la bonne modalité en temps réel
Mica unifie les modalités d’imagerie par lumière transmise et fluorescente. Au sein d'un Microhub, vous pouvez choisir parmi plusieurs modalités d’imagerie : champ large, confocal, imagerie THUNDER, LIGHTNING, Z-stacks, time-lapse et plus encore.
Ainsi, vous pouvez générer des aperçus rapides avec un champ large à faible grossissement, zoomer graduellement sur les régions d’intérêt et passer au confocal si nécessaire sans jamais déplacer l’échantillon vers un autre système.
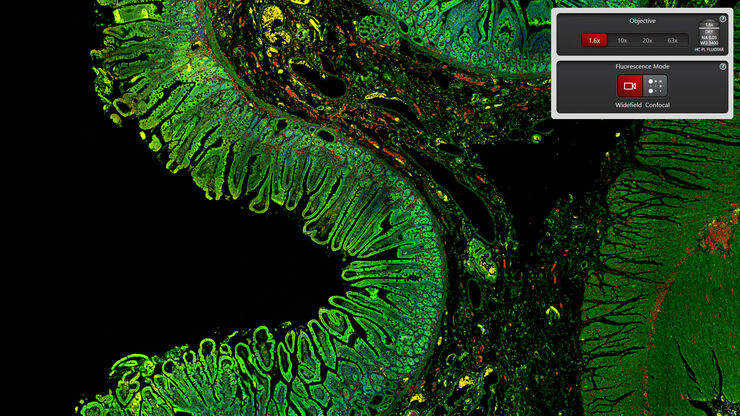
- Passez facilement d’un aperçu rapide à une haute résolution lorsque votre expérience l’exige
- Passez du mode champ large au mode confocal d’un simple clic sans déplacer votre échantillon
Aucune contrainte - Bénéficiez de conditions quasi-physiologiques tout au long de vos expériences
Les expériences de cellules vivantes exigent des cellules en forme optimale. En général, un contrôle de la température et du pH (via le CO2) dans l'environnement est nécessaire pour les cellules 2D et 3D dans un milieu. Des concentrations nutritionnelles et ioniques stables nécessitent une évaporation minimale. Certaines expériences exigent même que l’O2 soit proche des niveaux physiologiques. Mica peut fournir les conditions adéquates dans la configuration des cellules vivantes.
Workflows radicalement simplifiés
L’automatisation intelligente et l’analyse basée sur l’IA assurent une plus grande efficacité et un temps jusqu'à publication plus court.
- Réduction de plus de 60 % des étapes de processing grâce à l’intelligence du système
- Réduisez le temps et les efforts consacrés à l’analyse des échantillons en simplifiant l’ensemble de votre workflow
- Reproductibilité et répétabilité à 100 % tout au long de votre expérience
Découvrez Mica dans les applications clés
EN SAVOIR PLUS
Esperimenti MicaCam
MicaCam è il luogo in cui i ricercatori del settore delle scienze biologiche si riuniscono per confrontarsi e fare scoperte.
Guarda gli esperimenti scientifici pertinenti utilizzando Mica, il primo microhub al mondo.